“Não Vimos Tudo”: Pesquisa de USP e UFMG Desvenda Novas Famílias e Redefine o Quebra-Cabeça dos Vírus Gigantes na Virologia
Os vírus gigantes, descobertos no início dos anos 2000, continuam a ser uma fonte de surpresas para a virologia. Sua identificação já havia transformado o estudo da virosfera, revelando uma comunidade biológica até então desconhecida. Agora, um estudo liderado por pesquisadores da Escola Superior de Agricultura Luiz de Queiroz (ESALQ) da USP e da Universidade Federal de Minas Gerais (UFMG) revela mais uma faceta inexplorada desses organismos, propondo uma nova divisão dentro da família de vírus gigantes Asfarviridae.
A pesquisa indica que o que antes era considerado uma única família é, na verdade, composto por diversas linhagens distintas. “Há pelo menos cinco famílias diferentes dentro do que se pensava ser uma”, afirmou Luiz Eduardo Del Bem, professor do Departamento de Genética da ESALQ e autor correspondente do estudo. Segundo ele, a grande distância evolutiva entre os indivíduos sugere que a espécie deveria ser dividida em novas famílias, revelando que os vírus gigantes são compostos por “mais espécies e gêneros do que se imaginava”.
Os resultados, publicados no prestigiado periódico científico Journal of Virology, receberam duas importantes distinções: Editor’s Choice (concedido a cerca de 10% dos artigos) e “Gems” (destinado a apenas 1% das publicações com potencial para mudar paradigmas na virologia).
O que são e por que são tão intrigantes?
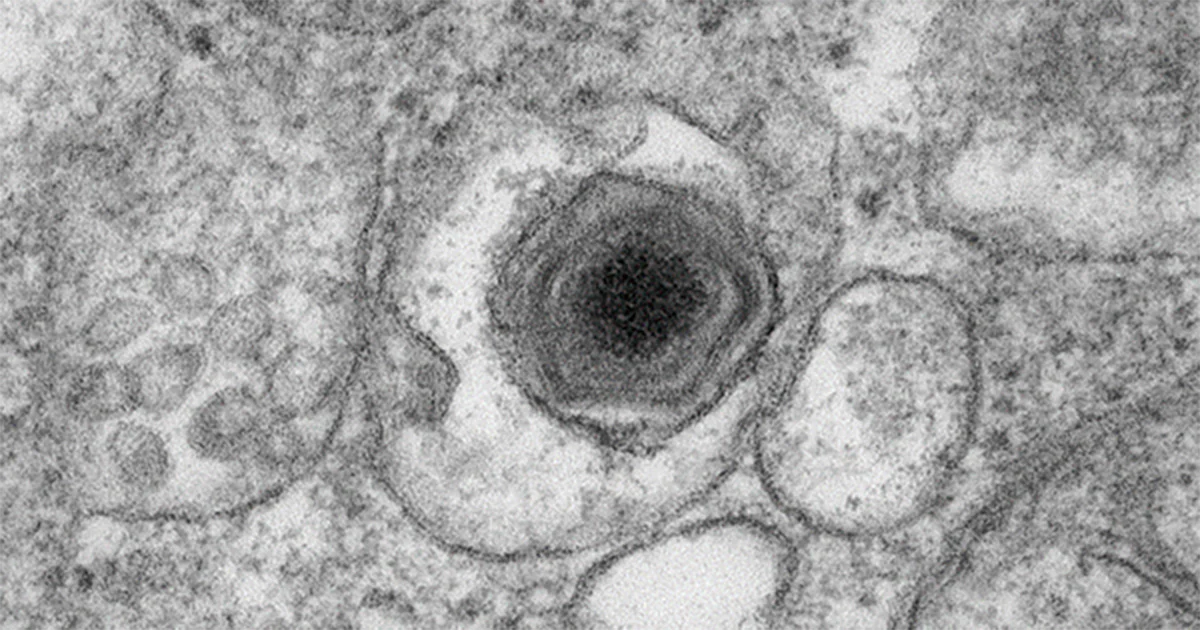
A descoberta dos vírus gigantes forçou a biologia a repensar suas categorias e a própria definição de ser vivo. Antes, os vírus eram vistos como entidades simples, parasitas obrigatórios e de tamanho diminuto. No entanto, os vírus gigantes são exceções notáveis. “Eles são outliers”, explica Thiago Mendonça-Santos, primeiro autor do artigo, destacando que seu tamanho é tão grande que, por vezes, são confundidos com bactérias. Um vírus gigante recém-descoberto pode atingir 2.600 nanômetros e possuir 867 genes, enquanto o coronavírus, por exemplo, tem 120 nanômetros e 11 genes.
Além do tamanho, a complexidade genética é impressionante. Metade dos genes desses vírus ainda não tem função conhecida pela ciência. O trabalho, fruto da pesquisa de doutorado de Mendonça-Santos, sugere uma diversidade muito maior do que a imaginada. Apesar dos avanços, Del Bem ressalta ao Jornal da USP que “ainda não se sabe exatamente o que eles são nem quais funções biológicas são capazes de realizar”.
Desvendando o quebra-cabeça com métodos inusitados
A descoberta tardia desses microrganismos se deu em parte por filtros que, antigamente, retinham os vírus gigantes junto com bactérias e outros microrganismos unicelulares maiores, impedindo sua análise. Mendonça-Santos também explica que, por serem majoritariamente ambientais e não infectarem humanos, esses vírus passaram despercebidos pela saúde pública.
Os vírus gigantes estudados, antes agrupados na mesma família Asfarviridae, infectam uma vasta gama de organismos, desde amebas até porcos, seus hospedeiros mais complexos. Essa ampla variedade já era um indício de diversidade oculta. Para desvendar essa questão, os pesquisadores aplicaram métodos incomuns: técnicas genômicas empregadas em botânica e no estudo de organismos multicelulares foram “importadas” para a virologia.
Analisando os 39 genomas completos disponíveis da família Asfarviridae, os pesquisadores identificaram 2.483 grupos de genes, dos quais apenas 37 estavam presentes em todos os vírus. Cerca de 40% dos genes ocorrem em apenas um único genoma, evidenciando uma enorme diversidade. Essa informação foi crucial para construir uma nova árvore filogenética, que revelou a divisão das linhagens e a distância evolutiva entre as espécies. “Esses vírus seguiram caminhos distintos, e isso precisa ser refletido na taxonomia”, pontuou Del Bem.
Novas propostas de classificação e o futuro da virologia
A classificação dos vírus é responsabilidade do Comitê Internacional de Taxonomia de Vírus (ICTV). O estudo agora propõe uma nova classificação, argumentando que manter todos os gigavírus previamente pertencentes à Asfarviridae na mesma família não faz mais sentido. Os dados apoiam uma reclassificação taxonômica em clados bem definidos.
A família Asfarviridae foi mantida, mas agora com apenas três espécies. Quatro novas famílias foram sugeridas: Faustoviridae (com quatro espécies), Kaumoebaviridae (com duas), Pacmanviridae (com duas) e Abaloneviridae (com um gênero descrito, mas ainda sem espécies identificadas). A separação foi definida com base na identidade genética – um índice calculado a partir de dados genômicos. Valores acima de 95% de similaridade sugerem a mesma espécie, até 70% o mesmo gênero e menos de 40% a mesma família. “Esses valores [para separação de clados] são arbitrários, mas são baseados em dados experimentais”, explicou Del Bem.
“Ao contrário de outros organismos, os vírus não possuem muitos critérios morfológicos que possam ser utilizados”, disse Del Bem. Identificar características genéticas é a solução para classificar as espécies. O estudo destaca que organizar o grupo é essencial para compreender o funcionamento e o impacto dos vírus gigantes no ambiente e nos organismos hospedeiros. “A cada novo genoma, genes completamente inéditos aparecem. Isso mostra que estamos lidando com um grupo cuja diversidade ainda é imensa”, concluiu o professor. Para Del Bem, o pangenoma desses vírus está em constante expansão, e muitas espécies ainda esperam ser descobertas: “Ainda não vimos tudo o que esses vírus têm a oferecer”.
Fonte: jornal.usp.br